
О подразделении
Лаборатория молекулярной генетики микробных консорциумов была создана на базе Академии биологии и биотехнологии им. Д.И. Ивановского ЮФУ в рамках молодежного блока исследовательских проектов университета в рамках программы «Приоритет 2030» и активно развивает перспективные направления в области генетики, микробиологии и биотехнологии.
В настоящее время лаборатория входит в стратегический проект «Системы управления почвенными ресурсами» Приоритета-2030, а также выполняет грант РНФ «Новые рекомбинантные штаммы и консорциумы споровых бактерий - основа биофунгицидных препаратов для агропромышленности» совместно с МФТИ.
Основные направления деятельности
-
Разработка методов культивирования новых, ранее некультвируемых микроорганизмов
Коллективом получено несколько патентов на среды и способы культивирования редких групп микроорганизмов из почвенных микробных сообществ. -
Исследование структуры и функций микробных сообществ
Лаборатория изучает особенности взаимодействия микроорганизмов в составе природных и искусственных консорциумов, анализируя их генетическое разнообразие, механизмы кооперации и конкуренции. -
Разработка генетических баз данных и моделей для машинного обучения
Использование методов современной геномики, биоинформатики, машинного обучения позволило коллективу создать нейросетевую модель для предсказания экологической роли микроорганизмов по геномным и метагеномным данным. В настоящее время (2025) коллектив работает над подходами к инженерии микробных сообществ in silico. -
Прикладные исследования для биотехнологии и экологии
Результаты исследований находят применение в создании новых биотехнологических решений для сельского хозяйства, в частности, разработке биопрепаратов для защиты растений. -
Образовательная и популяризаторская деятельность
Лаборатория активно вовлекает студентов и молодых ученых в научную работу и регулярно организует открытые семинары. Информация о текущих проектах, событиях и научных достижениях регулярно публикуется в официальном телеграм-канале лаборатории https://t.me/labmolgenmicr

Публикации
Все публикации, которые относятся к нашей лаборатории.
-
Demin K. et al. Alternative agar substitutes for culturing unculturable microorganisms //Archives of Microbiology. – 2024. – Т. 206. – №. 10. – С. 405.
-
Skripnichenko R. V. et al. Potential probiotic Bacillus strains with antioxidant and antimutagenic activity increased weight gain and altered hsp70, cxc, tnfα, il1β, and lysC gene expression in Clarias gariepinus //Fishes. – 2024. – Т. 9. – №. 12. – С. 476.
-
Demin K. A. et al. Sulfate-reducing bacteria unearthed: ecological functions of the diverse prokaryotic group in terrestrial environments //Applied and Environmental Microbiology. – 2024. – Т. 90. – №. 4. – С. e01390-23.
-
Statsenko V. N., Prazdnova E. V., Kulikov M. P. Influence of rifampicin-resistance mutations on the synthesis of antioxidant, DNA-protective, and SOS-inhibitory metabolites //Applied Biochemistry and Microbiology. – 2025. – Т. 61. – №. 3. – С. 542-550.
-
Bazhenov S. V., Novoyatlova U.S., Scheglova E.S., Prazdnova E.V. et al. Bacterial lux-biosensors: Constructing, applications, and prospects //Biosensors and Bioelectronics: X. – 2023. – V. 13. – P. 100323.
-
Churilov M. N., Prazdnova E. V., Rudoy D. V. Psychobiotics in Aquaculture: Harnessing the Microbiome–Gut–Brain Axis for Stress Management and Production Enhancement in Fish //Animals. – 2025. – V. 15. – №. 18. – P. 2726.
-
Demin K. A., Kulikova D. B., Kulikov M. P., Mazanko M. S., Prazdnova E. V. Gellan gum-based media recover more diverse microbial communities from soil material //Archives of Microbiology. – 2025. – V. 207. – №. 12. – P. 1-11.
-
Emelyantsev S., Prazdnova E., Chistyakov V. Solubilizer of bacterial origin surfactin increases the biological activity of C60 fullerene //Biotechnology and Applied Biochemistry. – 2025. – V. 72. – №. 2. – P. 311-319
-
Neurov A. M., Zaikina A. A., Prazdnova E. V. et al. Modulation of Stress-Related Protein in the African Catfish (Clarias gariepinus) Using Bacillus-Based Non-Ribosomal Peptides //Microbiology Research. – 2024. – V. 15. – №. 4. – P. 2743-2763
-
Prazdnova E. et al. Lipopeptides from Bacillus Probiotics Can Target Transmembrane Receptors NOX4, EGFR, PDGFR, and OCTN2 Involved in Oxidative Stress and Oncogenesis //BioTech. – 2026. – Т. 15. – №. 1. – С. 4.
-
Prazdnova E. V. et al. Genomic Analysis and Metabolite Profiling of Three Probiotic Bacillus Strains for Potential Application in Aquaculture //Preventive Nutrition and Food Science. – 2025. – V. 30. – №. 3. – P. 274.
-
Ranjan A., Rajput V.D., Prazdnova E.V. et al. Nature’s antimicrobial arsenal: non-ribosomal peptides from pgpb for plant pathogen biocontrol //Fermentation. – 2023. – V. 9. – №. 7. – P. 597.
-
Silina E. V. et al. Development of a Collagen–Cerium Oxide Nanohydrogel for Wound Healing: In Vitro and In Vivo Evaluation //Biomedicines. – 2025. – Т. 13. – №. 11. – С. 2623.
Наша команда
В составе коллектива — 80% исследователей младше 39 лет, в том числе аспиранты и студенты.
В 2024 г. сотрудники лаборатории выиграли конкурс «Старт-Взлет» и успешно открыли малое предприятие по разработке биопрепаратов.










Последние новости
-
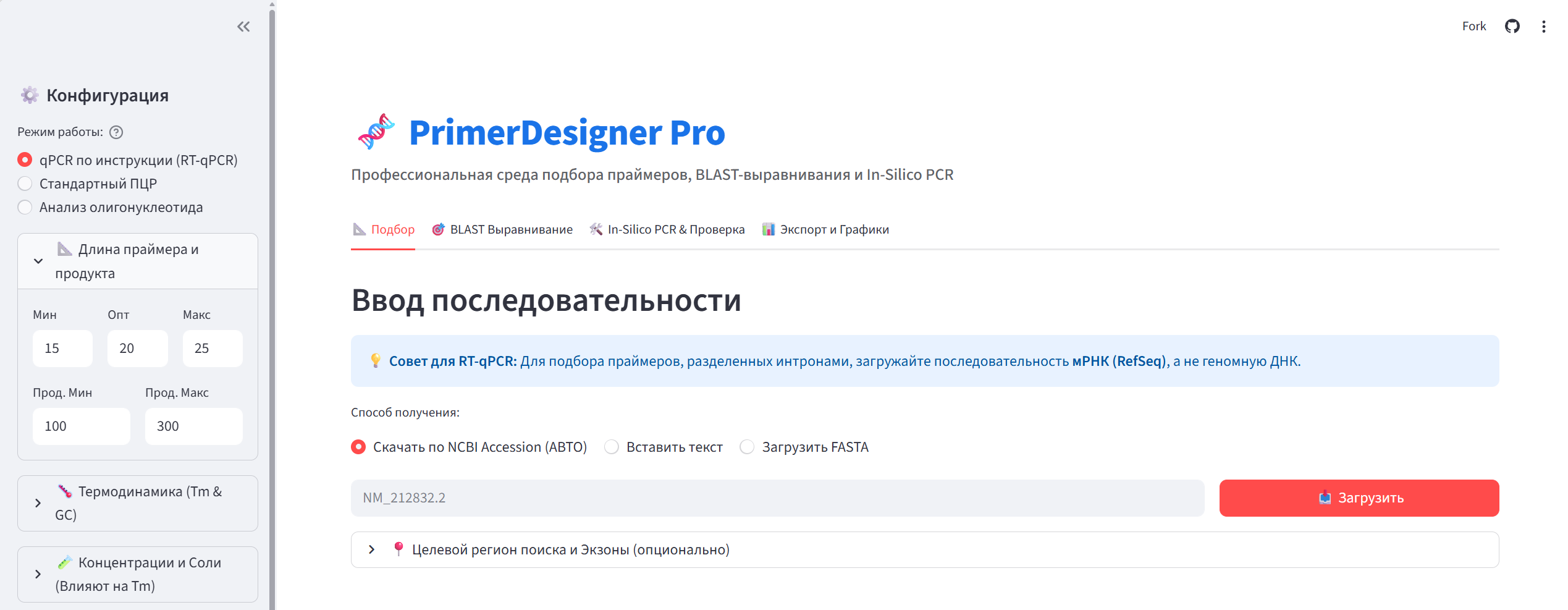 Представляем PrimerDesigner Pro: Универсальный веб-инструмент нашей лаборатории для дизайна и проверки праймеров
Представляем PrimerDesigner Pro: Универсальный веб-инструмент нашей лаборатории для дизайна и проверки праймеровКоллеги! Все мы знаем, насколько рутинным и долгим может быть процесс подбора качественных праймеров для ПЦР и, в особенности, для RT-qPCR. Бесконечное переключение между вкладками NCBI, ручной поиск координат экзонов, вчитывание в серый текст результатов BLAST и перенос последовательностей в сторонние программы вроде uGene для финальной проверки — всё это отнимает драгоценное время и повышает риск человеческой ошибки.
Мы решили это исправить. Рады представить вам PrimerDesigner Pro — новый веб-инструмент, разработанный в нашей лаборатории, который объединяет весь цикл работы с праймерами в одном удобном окне.
Приложение полностью автоматизирует золотой стандарт подбора праймеров (включая строгие требования для RT-qPCR) и делает работу с базами данных NCBI интуитивно понятной.
-
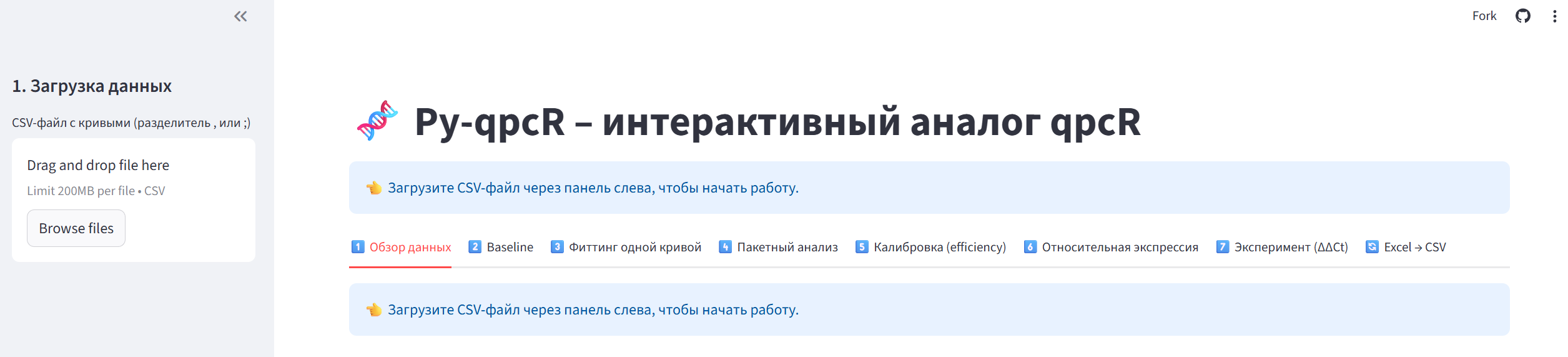 Запуск Py-qpcR: Наше новое веб-приложение для автоматизированного анализа данных RT-qPCR
Запуск Py-qpcR: Наше новое веб-приложение для автоматизированного анализа данных RT-qPCRУважаемые коллеги!
Мы рады представить Py-qpcR — новый интерактивный инструмент, разработанный специально для нашей лаборатории. Приложение призвано избавить исследователей от рутинных расчетов в Excel, сложных скриптов на R и вероятности «человеческой ошибки» при обработке сырых данных ПЦР в реальном времени.
Py-qpcR представляет собой современный веб-интерфейс, который берет на себя весь цикл обработки данных: от загрузки сырых флуоресцентных кривых до выдачи готовых значений Fold Change и статистической значимости (p-value). Инструмент базируется на надежных математических алгоритмах, аналогичных известному R-пакету
qpcR. -
 Встречайте StatPack OmniLab: Наша новая универсальная платформа для анализа научных данных
Встречайте StatPack OmniLab: Наша новая универсальная платформа для анализа научных данныхУважаемые коллеги!
Мы рады сообщить о запуске StatPack OmniLab — нашей собственной интерактивной веб-лаборатории для статистической обработки и визуализации данных.
Современная наука требует строгих доказательств и качественной визуализации для публикаций в высокорейтинговых журналах (Q1/Q2). До сих пор это означало необходимость осваивать сложное программирование на R / Python или покупать дорогие лицензии на Statistica.
Мы решили эту проблему. StatPack OmniLab берет всю рутину на себя: вы просто загружаете свой Excel-файл, а программа автоматически подбирает нужные тесты, строит профессиональные графики и генерирует отчеты. Без единой строчки кода!
https://stat11-new.streamlit.app/
Наши базы данных
Наши депонированные базы данных содержат уникальные наборы данных, созданные и собранные сотрудниками лаборатории в рамках научных исследований. Они доступны для ознакомления и использования в образовательных и исследовательских целях.
Наши инструменты
Наши инструменты содержат уникальные наборы данных, созданные и собранные сотрудниками лаборатории в рамках научных исследований.
Они доступны для ознакомления и использования в образовательных и исследовательских целях.
Контакты
Если у вас есть вопросы или предложения, пожалуйста, свяжитесь с нами по адресу prazdnova@sfedu.ru.
Наш адрес: г.Ростов-на-Дону, пр. Стачки 194/1
